Figure 3
Formation de l'oeil de réplication chez un procaryote
Lors de la publication de leur modèle, Watson et Crick avait fait remarquer que l’appariement complémentaire des bases suggérait un mécanisme de copie pour expliquer la reproduction du matériel génétique.
Il a été effectivement montré que la synthèse de la molécule d’ADN s’effectuait par autoduplication, ou réplication, selon un mode semi-conservatif de la molécule préexistante (Meselson et Stahl, 1958). Chaque brin de la double hélice sert de matrice pour la synthèse d’un brin complémentaire. A l’issue du processus, chacune des deux molécules filles est constituée d’un brin provenant de la molécule mère et d’un brin néosynthétisé.
De plus, comme tout processus de synthèse cellulaire, la réplication nécessite un système enzymatique qui catalyse les différentes réactions chimiques qui la constituent, et notamment une enzyme catalysant la polymérisation des désoxyribonucléotides : une ADN polymérase.
L’isolement d’une ADN polymérase a été réalisée
pour la première fois chez une bactérie : Escherichia coli. Il
existe en fait plusieurs types d’ADN polymérases dans les cellules,
y compris chez les procaryotes (polymérases I, II et III). Elles présentent
toutes des propriétés communes importantes : elles catalysent
la formation d’une liaison phosphodiester entre 2 désoxyribonucléotides
et permettent donc l’élongation d’un polydésoxyribonucléotide,
ceci dans les conditions suivantes :
- présence d’une matrice sous forme d’un ADN monocaténaire,
chaque nouveau nucléotide ajouté au brin en cours d’élongation
étant déterminé selon le principe de l’appariement
complémentaire des bases.
- la liaison ester se forme entre le phosphate du nucléotide ajouté
et la fonction alcool 3’ du polynucléotide. Cette propriété
a une conséquence importante : la croissance du brin en néoformation
ne peut se faire que dans le sens 5’? 3’.
- présence d’une chaîne de plusieurs nucléotides (ARN
ou ADN), appelée amorce, déjà appariée avec le brin
matrice. C’est donc à partir de l’extrémité
3’ OH de cette amorce que commence la polymérisation.
- les substrats de l’ADN polymérase sont les désoxyribonucléosides
triphosphates et non monophosphates. Elle catalyse donc la réaction suivante,
libératrice d’énergie :
Les ADN polymérases ne sont pas les seules enzymes à intervenir dans la réplication. D’autres activités enzymatiques sont nécessaires : hélicase, ATPases, primase, ligase.
En outre, des protéines dites SSB (Single Strand DNA BindingProteins) sont nécessaires.
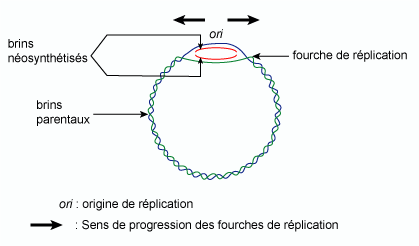
La réplication implique d’abord une séparation des deux brins de la molécule d’ADN (dénaturation de l’ADN), par rupture des liaisons hydrogène entre les bases complémentaires. Chez les procaryotes, ce processus est amorcé au niveau d’un site unique constitué d’une séquence de 250 paires de bases appelée origine de réplication (ori).
La rupture des liaisons hydrogène et donc la détorsion de la double hélice est catalysée par l’hélicase et est consommatrice d’énergie sous forme d’ATP, hydrolysé par des ATPases. La renaturation de l’ADN en amont de l’hélicase est contrecarrée par les protéines SSB. Chaque brin peut alors servir de matrice pour la synthèse d’un brin complémentaire, catalysée par l’ADN polymérase III.
Il se forme ainsi un œil de réplication constitué de deux fourches de réplication. La réplication est bidirectionnelle : elle progresse simultanément et en sens opposés sur chacune des fourches (figure 3).
Figure 3 |
 |
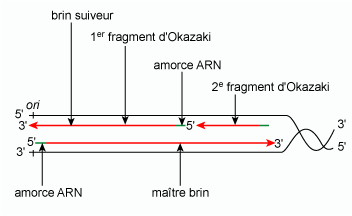
Les propriétés des ADN polymérases (voir § 3.2.1) ont deux conséquences importantes :
Figure 4 |
 |
Etant donné le caractère fondamental de la réplication de l’ADN, les grandes lignes du mécanisme décrit chez les procaryotes sont valables pour les eucaryotes.
Chez les eucaryotes, il existe plusieurs ADN polymérases nucléaires
et des ADN polymérases dans des organites comme les mitochondries et
les chloroplastes (voir chapitre 9 ).
Mais les différences essentielles avec la réplication chez les
procaryotes tiennent surtout à deux particularités de l’organisation
du génome des eucaryotes :
De plus les fragments d’Okazaki sont plus courts chez les eucaryotes (environ 200 nucléotides).
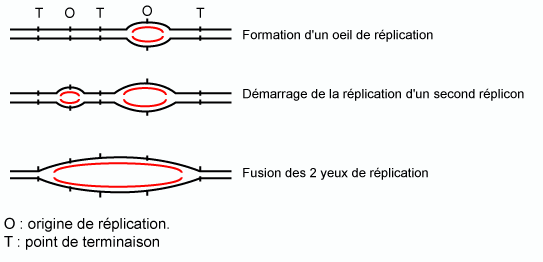
Par conséquent, s’il n’existait qu’une seule origine de réplication par chromosome, comme chez les procaryotes, il faudrait 800 heures pour répliquer une molécule d’ADN. La durée de réplication n’est en fait généralement que d’une heure ou deux. Chaque molécule d’ADN comporte plusieurs dizaines d’origines de réplication et donc autant d’ « unités de réplication » : les réplicons.
La longueur des réplicons est variable, de 30 000 à 300 000 pb. Tous ne fonctionnent pas en même temps. Seuls 20 p 100 d’entre eux sont actifs simultanément. La fusion des yeux de réplication contigus (figure 5) permet d’obtenir les deux molécules d’ADN qui, combinées aux histones, donneront chacune l’une des deux chromatides du chromosome.
Figure 5 |
 |